Rollen af restriktionsenzymer i moderne bioteknologi
Af Kay Tang – Opdateret 30. august 2022
Tidlig historie
I 1960'erne opdagede forskerne Werner Arber og Stewart Linn, at visse enzymer i E. coli kunne blokere viral replikation ved at spalte DNA. De identificerede en klasse af enzymer – senere betegnet restriktionsnukleaser – der skærer DNA i tilfældige positioner, hvilket understreger behovet for et mere præcist værktøj.
Bybrudsopdagelse
I 1968 isolerede H.O. Smith, K.W. Wilcox og T.J. Kelley det første velkarakteriserede restriktionsenzym, HindIII, ved Johns Hopkins University. HindIII skærer DNA ved en specifik 6-basepar-sekvens, en opdagelse, der åbnede døren til den systematiske brug af restriktionsenzymer i molekylærbiologi. Siden da er over 900 enzymer blevet identificeret fra 230 bakteriestammer, hvilket giver et stort værktøjssæt for videnskabsmænd.
Kortlægning af DNA
Restriktionsenzymer muliggør genomkortlægning gennem en teknik kaldet Restriction Fragment Length Polymorphism (RFLP). Ved at skære DNA på kendte genkendelsessteder genererer forskere fragmenter af karakteristiske længder, som kan adskilles ved gelelektroforese. RFLP har vist sig at være uvurderlig til DNA-typning, retsmedicinsk analyse og undersøgelse af genetisk variation i populationer.
Generering af rekombinant DNA
Hjørnestenen i genteknologi er skabelsen af rekombinante DNA-molekyler. I praksis skæres en plasmidvektor med et restriktionsenzym, og et gen af interesse - ofte afledt af en anden organisme - indsættes. De kompatible klæbrige ender produceret af Type II-enzymer forbindes af DNA-ligase og danner et stabilt hybridkromosom, der kan formeres i bakterier.
Typer af restriktionsenzymer
Restriktionsenzymer er kategoriseret i tre hovedklasser:
- TypeI genkender en specifik sekvens, men spalter kun den ene streng og kræver et separat enzym til at skære den anden streng, hvilket frigiver nukleotider på det afskårne sted.
- TypeII skær begge strenge ved eller nær genkendelsessekvensen, hvilket giver enten stumpe eller klæbrige ender, der er ideelle til kloning.
- TypeIII kløv begge strenge i en defineret afstand fra genkendelsesstedet, en egenskab, der er nyttig til visse analytiske anvendelser.
 Varme artikler
Varme artikler
-
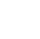
 Se det usete:Fødsel og død af trærødder under en fremtidig atmosfæreFelteksperimenter, der sporer roddynamik under kontrol og eCO2 betingelser. (A) BIFOR FACE-forsøgsanlægget er beliggende i modent løvskov nær Stafford, Storbritannien, og indeholder tre eCO2 (rød) og
Se det usete:Fødsel og død af trærødder under en fremtidig atmosfæreFelteksperimenter, der sporer roddynamik under kontrol og eCO2 betingelser. (A) BIFOR FACE-forsøgsanlægget er beliggende i modent løvskov nær Stafford, Storbritannien, og indeholder tre eCO2 (rød) og -
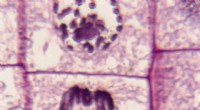 Omarrangering i Meiose:Hvordan kromosomal krydsning driver genetisk mangfoldighedDNA-omlejring, almindeligvis kendt som kromosomal crossover, er en kernecellulær mekanisme, der både reparerer DNA-skader og introducerer genetisk variation. Meiose Meiosis er den specialiserede afde
Omarrangering i Meiose:Hvordan kromosomal krydsning driver genetisk mangfoldighedDNA-omlejring, almindeligvis kendt som kromosomal crossover, er en kernecellulær mekanisme, der både reparerer DNA-skader og introducerer genetisk variation. Meiose Meiosis er den specialiserede afde -
 Eksotiske dyr og jagten på guldKredit:University of New Mexico Mænd, kvinder og deres familier ankom i stort tal til det nordlige Californien med drømmen om at blive rige i midten af det 19. århundrede. Hvad de fleste mennesk
Eksotiske dyr og jagten på guldKredit:University of New Mexico Mænd, kvinder og deres familier ankom i stort tal til det nordlige Californien med drømmen om at blive rige i midten af det 19. århundrede. Hvad de fleste mennesk -
 Atlanterhavsstørene opholder sigKredit:University of Maine Atlanterhavsstør den sommer i Maines Penobscot River-udmunding kan findes om efteråret og vinteren i farvande så langt væk som Nova Scotia og New York City, ifølge en sy
Atlanterhavsstørene opholder sigKredit:University of Maine Atlanterhavsstør den sommer i Maines Penobscot River-udmunding kan findes om efteråret og vinteren i farvande så langt væk som Nova Scotia og New York City, ifølge en sy
- 'Squishy' lasere kunne afsløre, hvordan tumorer og babyer vokser
- Ny forskning identificerer mønstre for træfordeling i afrikanske savanner
- Bonoboer og chimpanser:Hvad vores nærmeste slægtninge fortæller os om mennesker
- Hvad er processen med at slidte klipper ved naturlige processer?
- Vil du slukke for min skærm spare energi?
- Undersøgelse viser, at kvindelig ledelse påvirker lønforskellene og virksomhedens præstationer